Side Menu
PBRM1
基本情報
- 遺伝子名
-
polybromo 1
- 慣用名
-
BAF180, PB1
- 遺伝子分類
-
がん抑制遺伝子
- 遺伝子ID
- 転写産物ID
- 機能分類
-
エピジェネティック制御
- シグナル伝達経路
-
Epigenetic modification
- 染色体上の位置 (GRCh37/hg19)
-
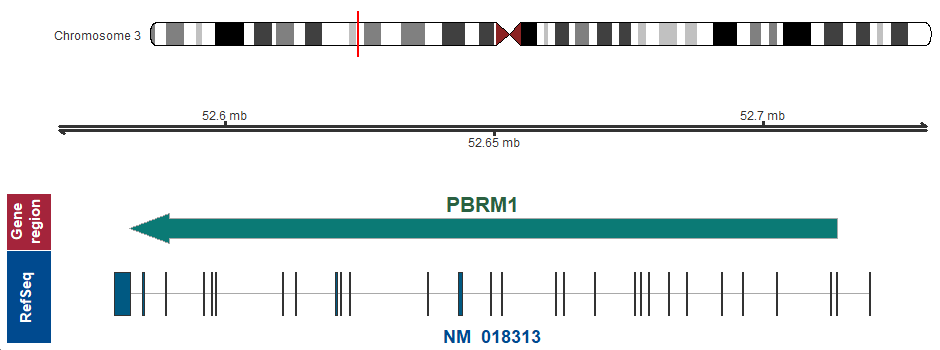
3p21.1 (chr3:52582079..52713727, complement)
- アミノ酸配列の長さ
-
1,582
遺伝子マップ
解説
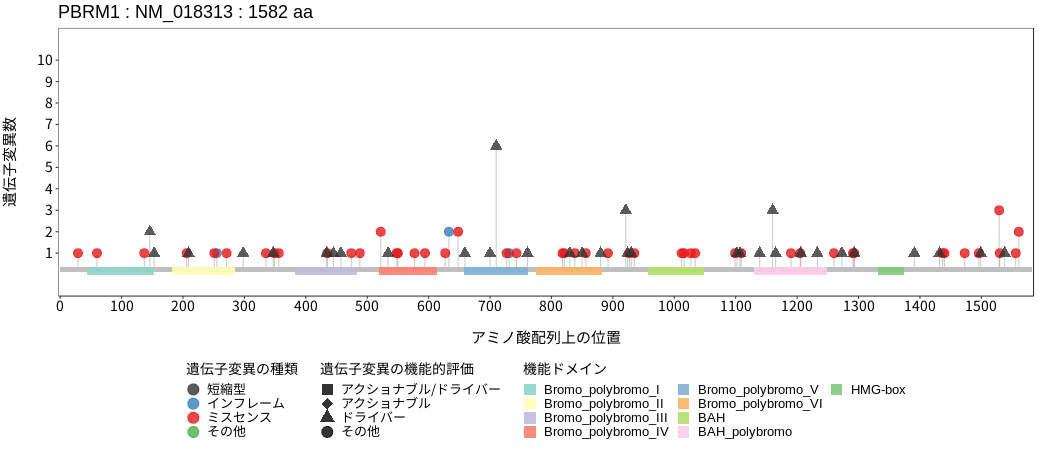
PBRM1 (BAF180)は、SWI/SNFクロマチンリモデリング複合体の構成分子である。クロマチンリモデリング複合体は、ATP依存的にクロマチン構造を変化させることで、転写制御因子などDNA結合タンパク質の標的DNA領域への結合を制御し、転写・複製および修復に関与する。PBRM1は、TP53の細胞老化および、細胞周期の調節に働くp21の発現調節に関与することが知られている。PBRM1は、BAP1およびARID1Aと共に胆道癌で高い頻度で変異が認められるクロマチンリモデリング関連の遺伝子であり、その大部分が機能喪失につながる可能性の高い短縮型変異である。
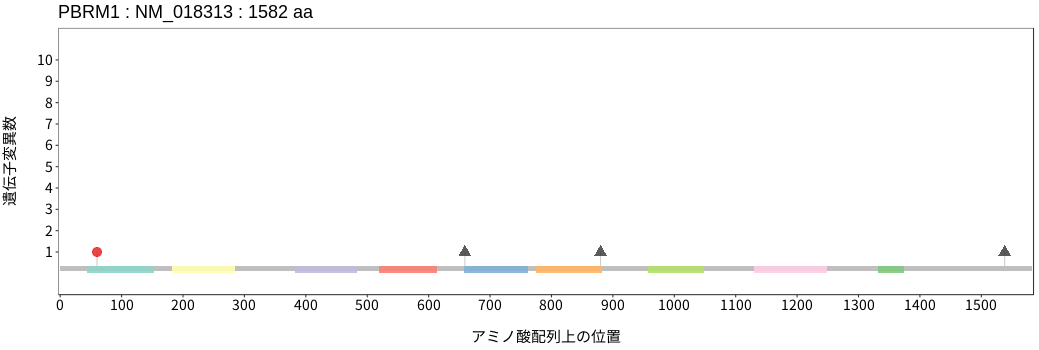
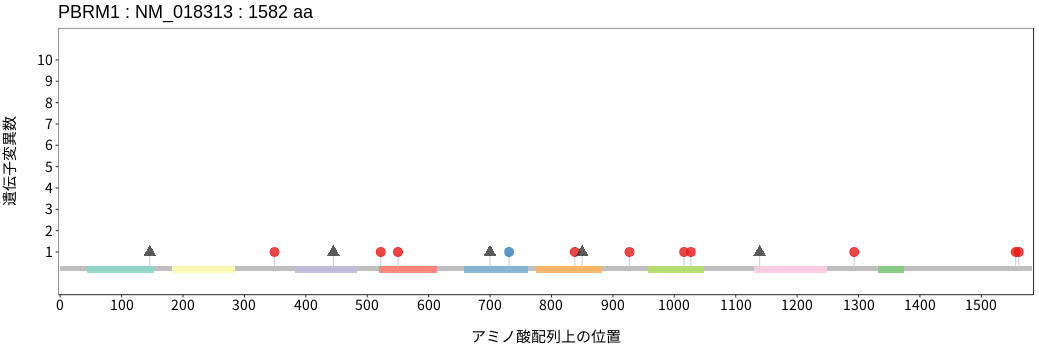
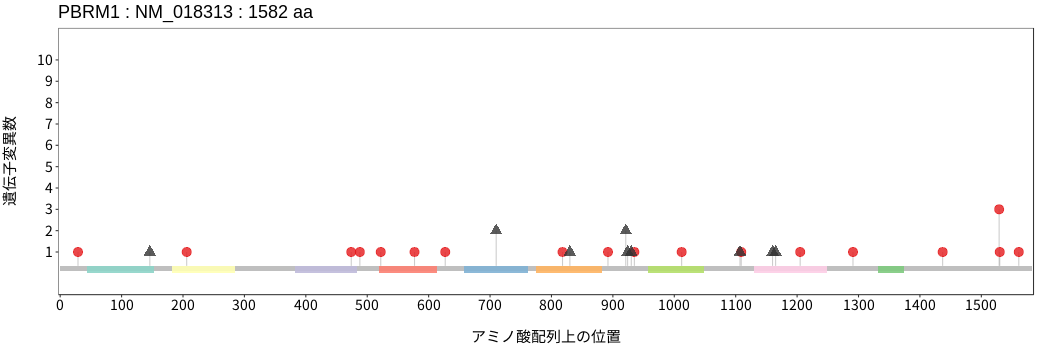
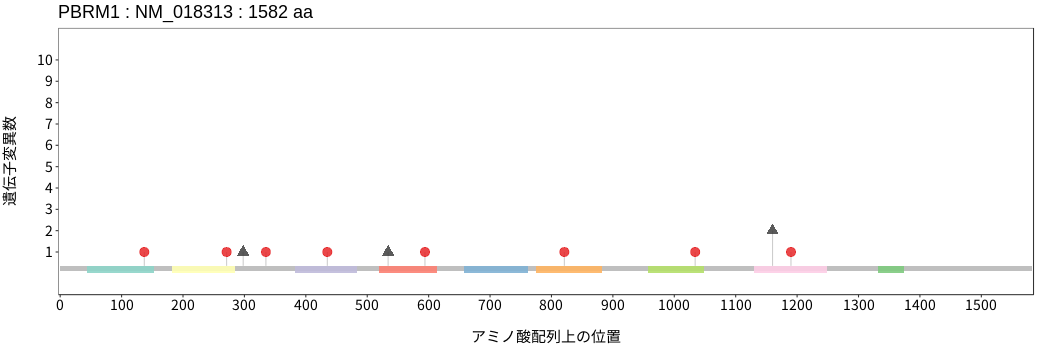
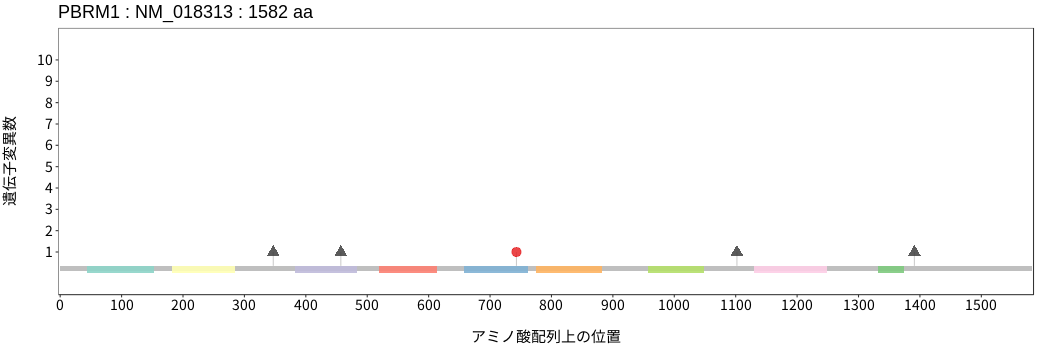
遺伝子変異総量(Tumor Mutation Burden)の分布TMB

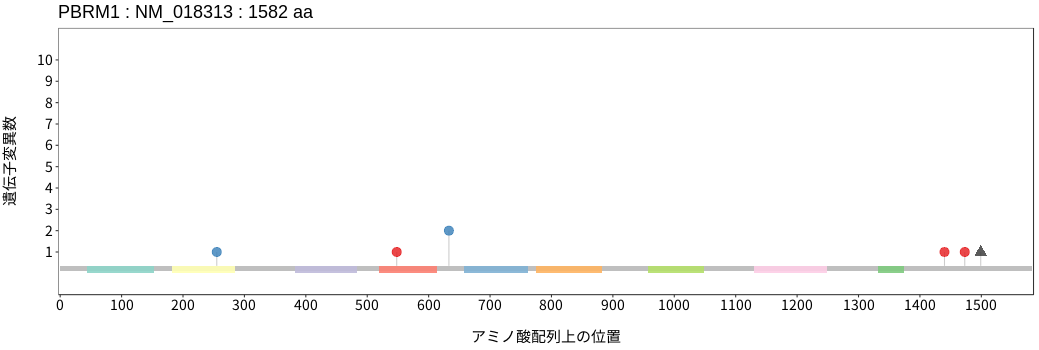
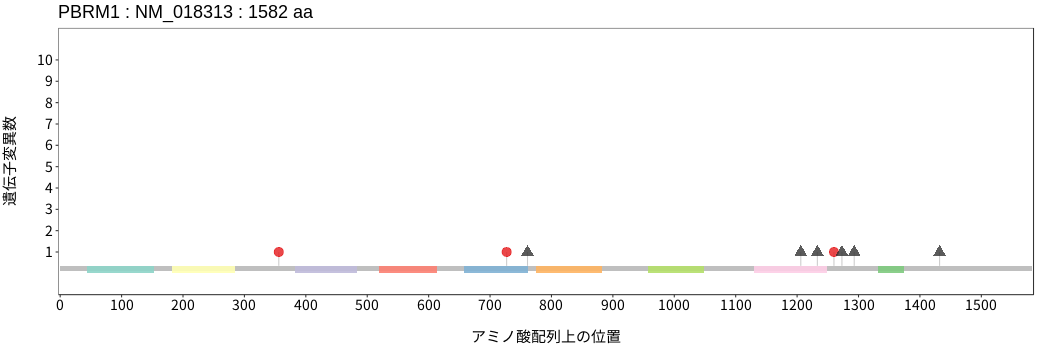
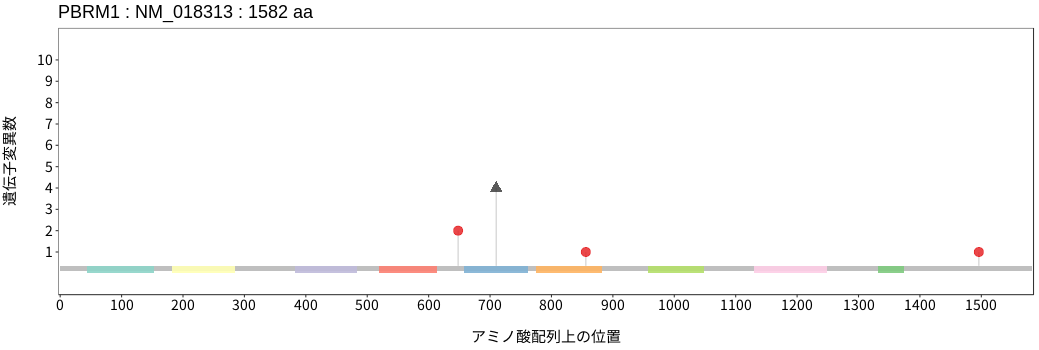
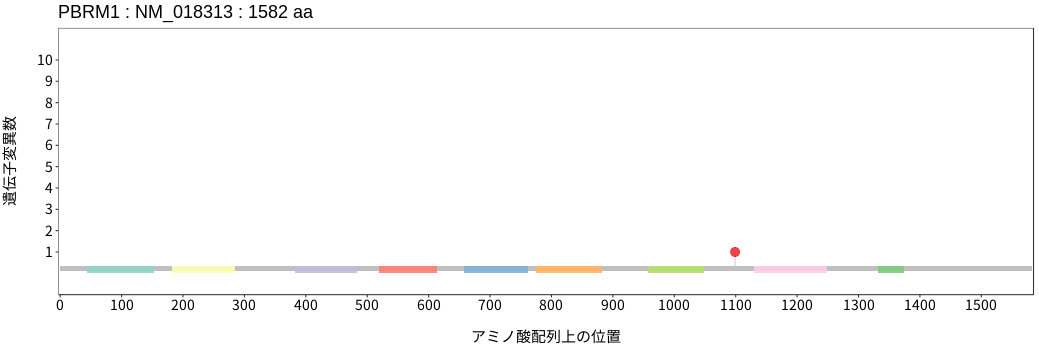
アミノ酸配列上の変異分布
- 低悪性度
神経膠腫 - 多形膠芽腫
- 髄膜腫
- 頭頸部
扁平上皮癌 - 唾液腺癌
- 食道扁平上皮癌
- 胃腺癌
- 小腸癌
- 結腸腺癌
- 直腸腺癌
- 肝細胞癌
- 胆管癌
- 膵腺癌
- 肺腺癌
- 肺扁平上皮癌
- 肺
神経内分泌腫瘍 - 胸膜中皮腫
- 胸腺腫
- 浸潤性乳管癌
- 浸潤性小葉癌
- 化生癌
- 骨肉腫
- 消化管間質腫瘍
- 軟部肉腫
- 子宮頸癌
- 子宮類内膜腺癌
- 上皮性卵巣癌
- 淡明細胞型
腎細胞癌 - 悪性黒色腫
- 有棘細胞癌
ドライバー変異リスト
| 参照配列上の 位置 (GRCh37/hg19) |
参照配列の塩基 | 変異の塩基 | 変異が位置するエクソン番号 | 変異 (アミノ酸 変化) |
変異 (CDS 変化) |
COSMIC登録ID (v92) | がん化との 関連度による 分類 |
変異が検出されたサンプル数 |
|---|---|---|---|---|---|---|---|---|
| chr3:52696220 | G | A | 5 / 30 | p.Q153* | c.457C>T | COSV56303401 | Tier2 | 1 / 113 |
| chr3:52696241 | G | A | 5 / 30 | p.R146* | c.436C>T | COSV56288194 | Tier2 | 2 / 113 |
| chr3:52692235 | G | A | 6 / 30 | p.Q209* | c.625C>T | COSV56262814 | Tier2 | 1 / 113 |
| chr3:52678727 | G | A | 9 / 30 | p.R298* | c.892C>T | COSV56261697 | Tier2 | 1 / 113 |
| chr3:52676016 | CA | C | 11 / 30 | p.M347fs | c.1040delT | Tier2 | 1 / 113 | |
| chr3:52668619 | G | A | 12 / 30 | p.R434* | c.1300C>T | COSV56260075 | Tier2 | 1 / 113 |
| chr3:52662984 | C | A | 13 / 30 | p.E457* | c.1369G>T | COSV56280985 | Tier2 | 1 / 113 |
| chr3:52663018 | TAA | T | 13 / 30 | p.L445fs | c.1333_1334delTT | Tier2 | 1 / 113 | |
| chr3:52651496 | G | A | 15 / 30 | p.R534* | c.1600C>T | COSV56261082 | Tier2 | 1 / 113 |
| chr3:52643348 | G | A | 17 / 30 | p.R850* | c.2548C>T | COSV56273176 | Tier2 | 1 / 113 |
| chr3:52643408 | C | A | 17 / 30 | p.E830* | c.2488G>T | Tier2 | 1 / 113 | |
| chr3:52643615 | T | A | 17 / 30 | p.R761* | c.2281A>T | Tier2 | 1 / 113 | |
| chr3:52643768 | G | A | 17 / 30 | p.R710* | c.2128C>T | COSV56260264 | Tier2 | 6 / 113 |
| chr3:52643796 | AAT | A | 17 / 30 | p.I700fs | c.2098_2099delAT | Tier2 | 1 / 113 | |
| chr3:52643921 | G | A | 17 / 30 | p.Q659* | c.1975C>T | Tier2 | 1 / 113 | |
| chr3:52637546 | C | A | 18 / 30 | p.E924* | c.2770G>T | COSV56273269 | Tier2 | 1 / 113 |
| chr3:52637555 | G | A | 18 / 30 | p.R921* | c.2761C>T | COSV56262126 | Tier2 | 3 / 113 |
| chr3:52637676 | GC | G | 18 / 30 | p.C880fs | c.2639delG | Tier2 | 1 / 113 | |
| chr3:52623261 | CTT | C | 19 / 30 | p.K930fs | c.2788_2789delAA | Tier2 | 1 / 113 | |
| chr3:52620448 | AAG | A | 21 / 30 | p.L1102fs | c.3303_3304delCT | Tier2 | 1 / 113 | |
| chr3:52613111 | GAC | G | 22 / 30 | p.V1139fs | c.3415_3416delGT | Tier2 | 1 / 113 | |
| chr3:52613209 | C | A | 22 / 30 | p.E1107* | c.3319G>T | COSV56265618 | Tier2 | 1 / 113 |
| chr3:52610557 | C | A | 23 / 30 | p.G1206* | c.3616G>T | COSV56309324 | Tier2 | 1 / 113 |
| chr3:52610678 | A | C | 23 / 30 | p.Y1165* | c.3495T>G | Tier2 | 1 / 113 | |
| chr3:52610695 | G | A | 23 / 30 | p.R1160* | c.3478C>T | COSV56264314 | Tier2 | 3 / 113 |
| chr3:52598169 | C | A | 24 / 30 | p.E1233* | c.3697G>T | Tier2 | 1 / 113 | |
| chr3:52597433 | C | A | 25 / 30 | p.E1293* | c.3877G>T | Tier2 | 1 / 113 | |
| chr3:52597493 | G | A | 25 / 30 | p.Q1273* | c.3817C>T | COSV56270502 | Tier2 | 1 / 113 |
| chr3:52588857 | G | A | 27 / 30 | p.Q1391* | c.4171C>T | Tier2 | 1 / 113 | |
| chr3:52584827 | A | AT | 28 / 30 | p.M1432fs | c.4294dupA | Tier2 | 1 / 113 | |
| chr3:52584512 | CTGAG | C | 29 / 30 | p.H1499fs | c.4497_4500delCTCA | COSV56305977 | Tier2 | 1 / 113 |
| chr3:52582217 | C | CTT | 30 / 30 | p.E1538fs | c.4610_4611insAA | Tier2 | 1 / 113 |