Side Menu
PTEN
基本情報
- 遺伝子名
-
phosphatase and tensin homolog
- 慣用名
-
BZS, CWS1, DEC, GLM2, MHAM, MMAC1, PTEN1, PTENbeta, TEP1
- 遺伝子分類
-
がん抑制遺伝子
- 遺伝子ID
- 転写産物ID
- 機能分類
-
腫瘍形成・増殖
- シグナル伝達経路
-
PI3K/Akt/mTOR
- 染色体上の位置 (GRCh37/hg19)
-
10q23.31 (chr10:89624227..89725229)
- アミノ酸配列の長さ
-
403
遺伝子マップ
解説
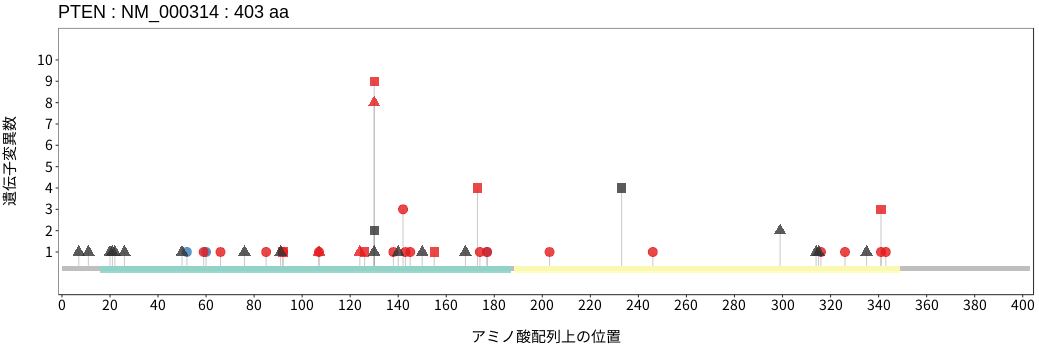
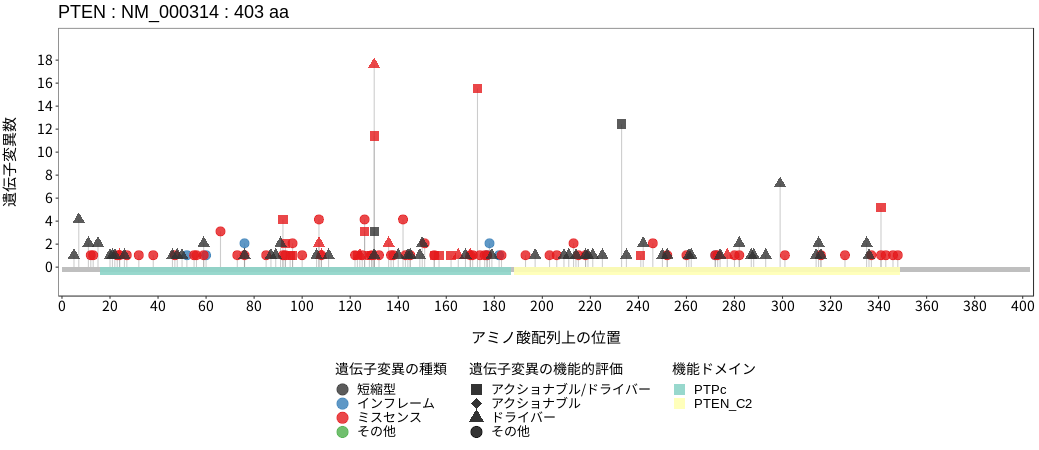
PTENは細胞膜上のホスファチジルイノシトール3,4,5-三リン酸[PI(3,4,5)P3]を脱リン酸化して、ホスファチジルイノシトール4,5-二リン酸 [PI(4,5)P2]に変換するホスファターゼである。この反応はホスファチジルイノシトール-3キナーゼ (PI3K)の逆反応であり、細胞増殖や運動性の亢進につながるPI3K/Akt/mTORシグナル経路の活性を抑制する。加えて、DNA二本鎖切断時の修復機構である相同組み換えの主要分子RAD51の発現調節に核内のPTENが関与していることが報告されている。そのため、PTENの機能喪失はPI3K/Akt/mTORシグナル経路の活性化だけでなく、ゲノムの不安定性につながる可能性が考えられる。多くのがん種において体細胞バリアントが検出されており、機能喪失の原因と成り得るフレームシフトバリアントやナンセンスバリアントに加えて130および173番目のアミノ酸(共にアルギニン)にホットスポットがあり、この部位のミスセンスバリアントはPTENの機能喪失につながることが知られている。生殖細胞系列バリアントは常染色体優性遺伝の疾患であるCowden症候群に代表されるPTEN過誤腫症候群 (PTEN Hamartoma Tumor Syndrome: PHTS) との関連が知れられている。
シグナル伝達経路

遺伝子変異総量(Tumor Mutation Burden)の分布TMB

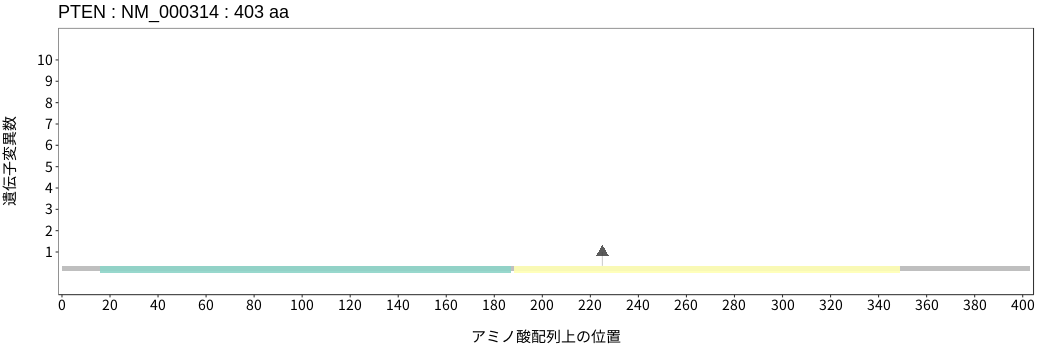
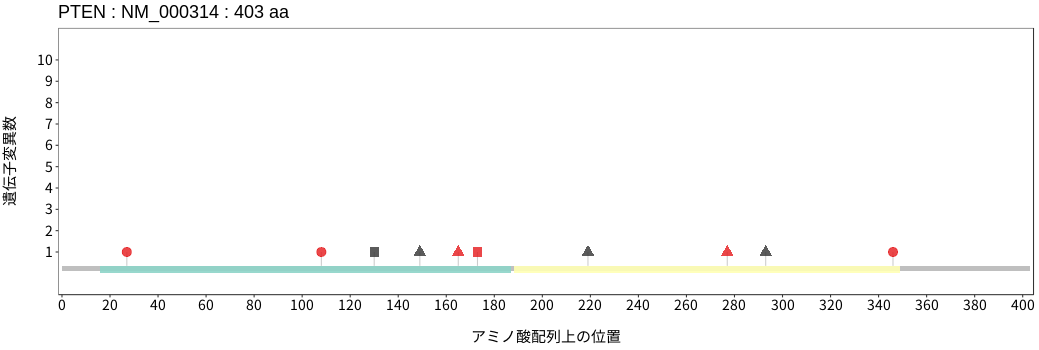
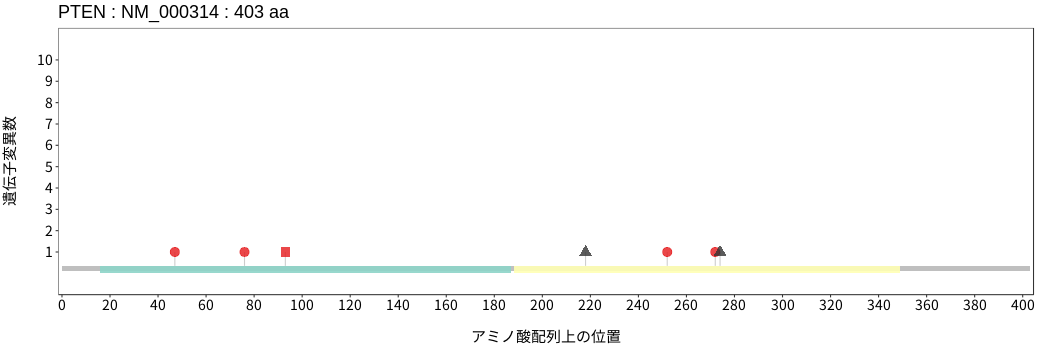
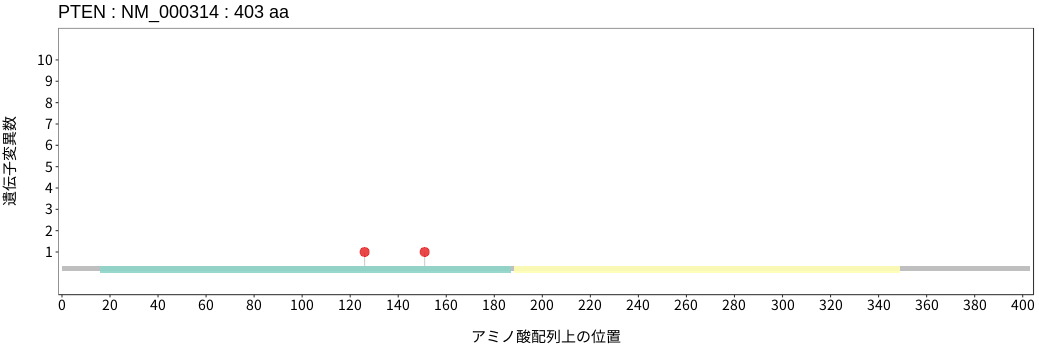
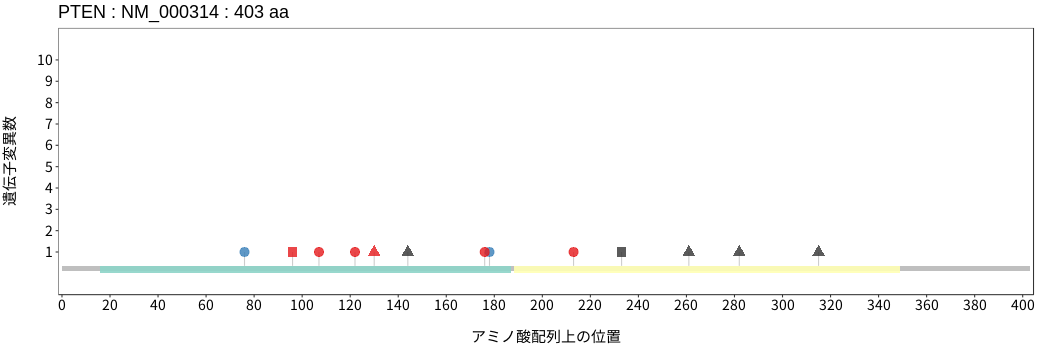
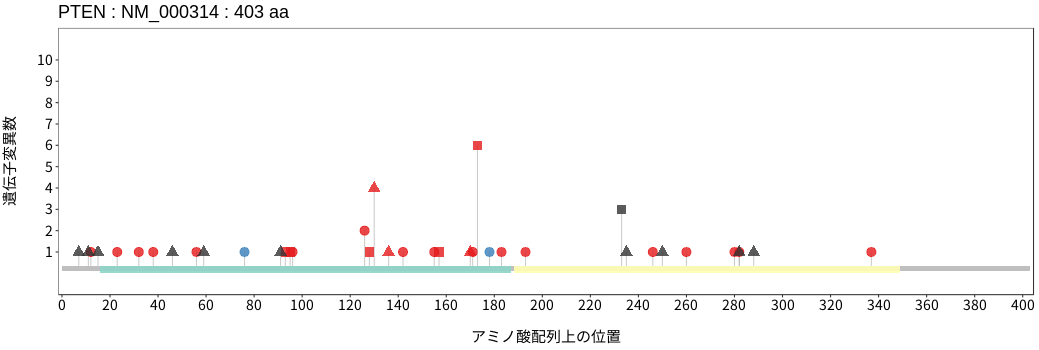
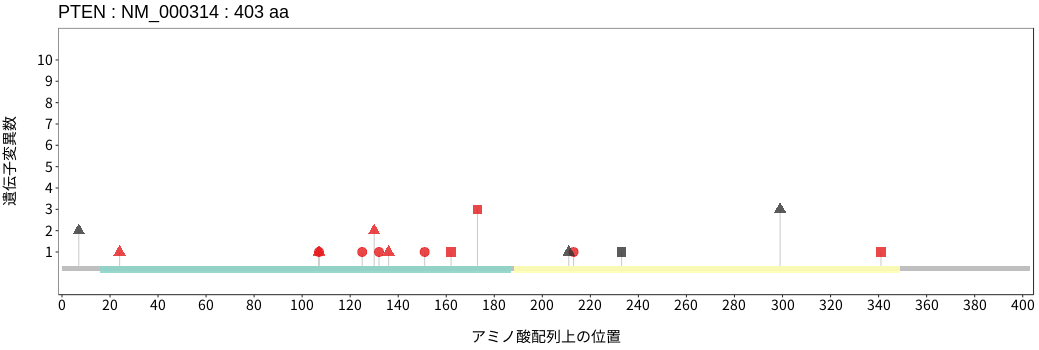
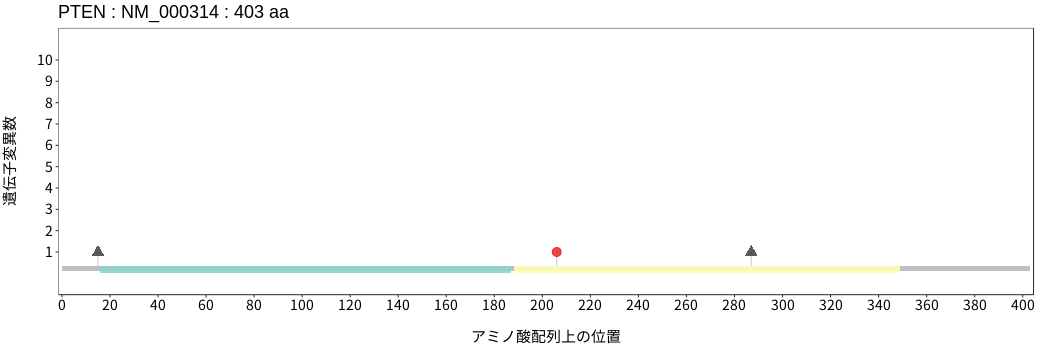
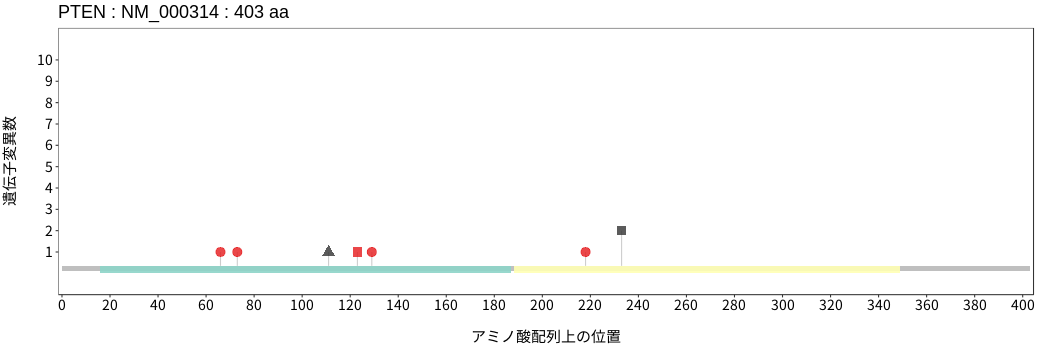
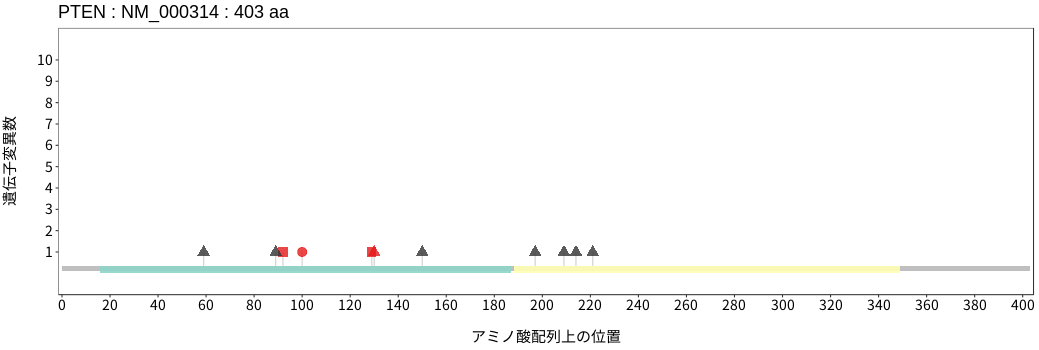
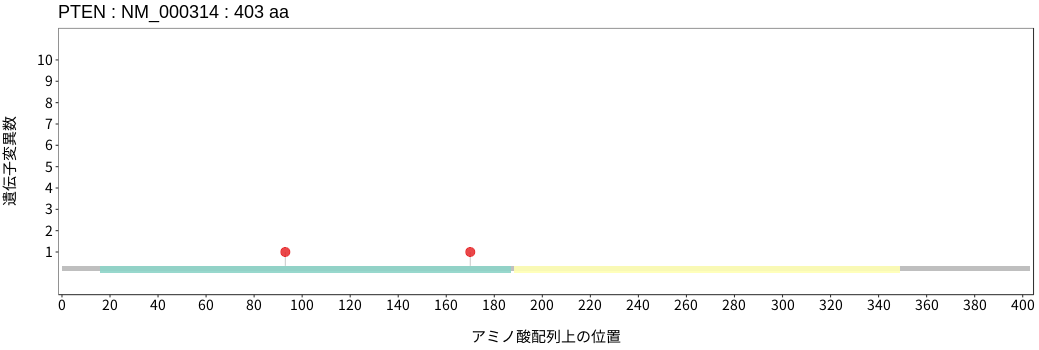
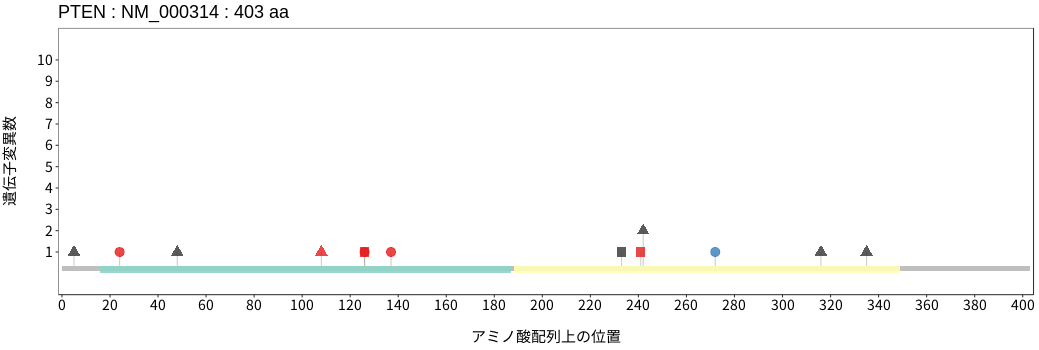
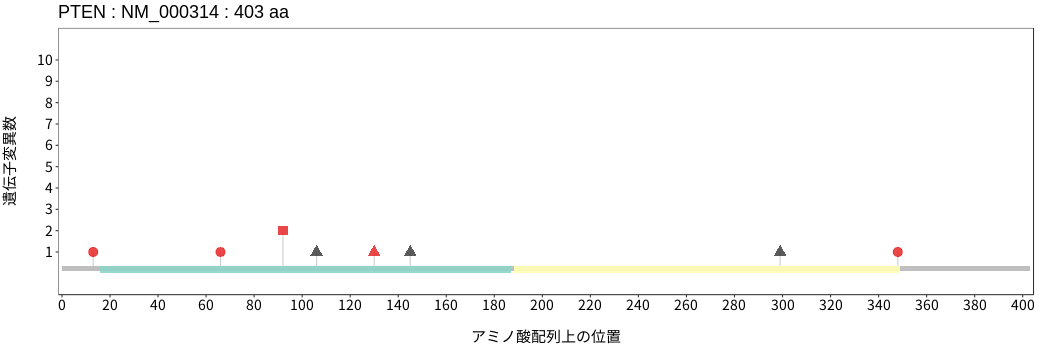
アミノ酸配列上の変異分布
- 低悪性度
神経膠腫 - 多形膠芽腫
- 髄膜腫
- 頭頸部
扁平上皮癌 - 唾液腺癌
- 食道扁平上皮癌
- 胃腺癌
- 小腸癌
- 結腸腺癌
- 直腸腺癌
- 肝細胞癌
- 胆管癌
- 膵腺癌
- 肺腺癌
- 肺扁平上皮癌
- 肺
神経内分泌腫瘍 - 胸膜中皮腫
- 胸腺腫
- 浸潤性乳管癌
- 浸潤性小葉癌
- 化生癌
- 骨肉腫
- 消化管間質腫瘍
- 軟部肉腫
- 子宮頸癌
- 子宮類内膜腺癌
- 上皮性卵巣癌
- 淡明細胞型
腎細胞癌 - 悪性黒色腫
- 有棘細胞癌
ドライバー変異リスト
| 参照配列上の 位置 (GRCh37/hg19) |
参照配列の塩基 | 変異の塩基 | 変異が位置するエクソン番号 | 変異 (アミノ酸 変化) |
変異 (CDS 変化) |
COSMIC登録ID (v92) | がん化との 関連度による 分類 |
変異が検出されたサンプル数 |
|---|---|---|---|---|---|---|---|---|
| chr10:89624240 | TCAAA | T | 1 / 9 | p.I5fs | c.15_18delCAAA | Tier2 | 1 / 218 | |
| chr10:89624245 | G | T | 1 / 9 | p.E7* | c.19G>T | COSV64288471 | Tier2 | 4 / 218 |
| chr10:89624255 | G | GC | 1 / 9 | p.R11fs | c.30dupC | Tier2 | 1 / 218 | |
| chr10:89624257 | AG | A | 1 / 9 | p.R11fs | c.32delG | Tier2 | 1 / 218 | |
| chr10:89624261 | ACAAAAGGAGATAT | A | 1 / 9 | p.R15fs | c.39_51delAAGGAGATATCAA | Tier2 | 1 / 218 | |
| chr10:89624265 | AAGGAGATATCAAG | A | 1 / 9 | p.R15fs | c.44_56delGATATCAAGAGGA | Tier2 | 1 / 218 | |
| chr10:89624279 | A | AGGAT | 1 / 9 | p.F21fs | c.58_61dupGGAT | Tier2 | 1 / 218 | |
| chr10:89624282 | A | AT | 1 / 9 | p.G20fs | c.57dupT | Tier2 | 1 / 218 | |
| chr10:89624290 | GA | G | 1 / 9 | p.D22fs | c.65delA | Tier2 | 1 / 218 | |
| chr10:89624296 | G | A | 1 / 9 | p.D24N | c.70G>A | COSV64295411 | Tier2 | 1 / 218 |
| chr10:89624297 | A | AC | 1 / 9 | p.T26fs | c.72dupC | COSV64303628 | Tier2 | 1 / 218 |
| chr10:89653831 | A | AGGCGT | 2 / 9 | p.Y46fs | c.130_134dupGGCGT | Tier2 | 1 / 218 | |
| chr10:89653845 | AC | A | 2 / 9 | p.N48fs | c.144delC | Tier2 | 1 / 218 | |
| chr10:89653849 | TATTG | T | 2 / 9 | p.I50fs | c.150_153delTGAT | Tier2 | 1 / 218 | |
| chr10:89685281 | C | G | 3 / 9 | p.S59* | c.176C>G | COSV64296058 | Tier2 | 1 / 218 |
| chr10:89685281 | C | A | 3 / 9 | p.S59* | c.176C>A | COSV64294267 | Tier2 | 1 / 218 |
| chr10:89690821 | T | G | 4 / 9 | p.Y76* | c.228T>G | COSV64307557 | Tier2 | 1 / 218 |
| chr10:89692775 | C | T | 5 / 9 | p.Q87* | c.259C>T | COSV64289438 | Tier2 | 1 / 218 |
| chr10:89692779 | A | AT | 5 / 9 | p.P89fs | c.264dupT | Tier2 | 1 / 218 | |
| chr10:89692786 | TG | T | 5 / 9 | p.E91fs | c.271delG | Tier2 | 1 / 218 | |
| chr10:89692787 | G | T | 5 / 9 | p.E91* | c.271G>T | COSV64292991 | Tier2 | 1 / 218 |
| chr10:89692790 | G | C | 5 / 9 | p.D92H | c.274G>C | COSV64295612 | Tier1 | 1 / 218 |
| chr10:89692791 | A | T | 5 / 9 | p.D92V | c.275A>T | COSV64302611 | Tier1 | 1 / 218 |
| chr10:89692791 | A | G | 5 / 9 | p.D92G | c.275A>G | COSV64288500 | Tier1 | 1 / 218 |
| chr10:89692792 | C | A | 5 / 9 | p.D92E | c.276C>A | COSV64288954 | Tier1 | 1 / 218 |
| chr10:89692793 | C | T | 5 / 9 | p.H93Y | c.277C>T | COSV64289544 | Tier1 | 1 / 218 |
| chr10:89692794 | A | G | 5 / 9 | p.H93R | c.278A>G | COSV64296545 | Tier1 | 1 / 218 |
| chr10:89692800 | C | T | 5 / 9 | p.P95L | c.284C>T | COSV64288477 | Tier1 | 1 / 218 |
| chr10:89692803 | C | A | 5 / 9 | p.P96Q | c.287C>A | COSV64296626 | Tier1 | 1 / 218 |
| chr10:89692832 | G | T | 5 / 9 | p.E106* | c.316G>T | COSV100910130 | Tier2 | 1 / 218 |
| chr10:89692835 | G | T | 5 / 9 | p.D107Y | c.319G>T | COSV64296475 | Tier2 | 2 / 218 |
| chr10:89692839 | T | C | 5 / 9 | p.L108P | c.323T>C | COSV64296046 | Tier2 | 1 / 218 |
| chr10:89692849 | G | A | 5 / 9 | p.W111* | c.333G>A | COSV64289174 | Tier2 | 1 / 218 |
| chr10:89692883 | C | G | 5 / 9 | p.H123D | c.367C>G | COSV64294365 | Tier1 | 1 / 218 |
| chr10:89692886 | T | A | 5 / 9 | p.C124S | c.370T>A | COSV64288968 | Tier2 | 1 / 218 |
| chr10:89692892 | G | T | 5 / 9 | p.A126S | c.376G>T | COSV64296979 | Tier1 | 1 / 218 |
| chr10:89692893 | C | A | 5 / 9 | p.A126D | c.377C>A | COSV64290343 | Tier1 | 1 / 218 |
| chr10:89692893 | C | G | 5 / 9 | p.A126G | c.377C>G | COSV64290444 | Tier1 | 1 / 218 |
| chr10:89692900 | G | T | 5 / 9 | p.K128N | c.384G>T | COSV64289333 | Tier1 | 1 / 218 |
| chr10:89692901 | G | A | 5 / 9 | p.G129R | c.385G>A | COSV64288557 | Tier1 | 1 / 218 |
| chr10:89692904 | C | G | 5 / 9 | p.R130G | c.388C>G | COSV64288384 | Tier1 | 11 / 218 |
| chr10:89692904 | C | T | 5 / 9 | p.R130* | c.388C>T | COSV64288463 | Tier1 | 3 / 218 |
| chr10:89692904 | CG | C | 5 / 9 | p.R130fs | c.389delG | COSV64290765 | Tier2 | 1 / 218 |
| chr10:89692905 | G | A | 5 / 9 | p.R130Q | c.389G>A | COSV64288376 | Tier1 | 17 / 218 |
| chr10:89692922 | T | C | 5 / 9 | p.C136R | c.406T>C | COSV64289087 | Tier1 | 2 / 218 |
| chr10:89692935 | T | G | 5 / 9 | p.L140* | c.419T>G | COSV64289095 | Tier2 | 1 / 218 |
| chr10:89692945 | C | CAT | 5 / 9 | p.K144fs | c.430_431insTA | Tier2 | 1 / 218 | |
| chr10:89692949 | TTTTTAAAGGC | T | 5 / 9 | p.F145fs | c.434_443delTTTTAAAGGC | Tier2 | 1 / 218 | |
| chr10:89692961 | C | T | 5 / 9 | p.Q149* | c.445C>T | COSV64288740 | Tier2 | 1 / 218 |
| chr10:89692964 | G | T | 5 / 9 | p.E150* | c.448G>T | COSV64289396 | Tier2 | 2 / 218 |
| chr10:89692980 | A | G | 5 / 9 | p.Y155C | c.464A>G | COSV64291751 | Tier1 | 1 / 218 |
| chr10:89692986 | A | G | 5 / 9 | p.E157G | c.470A>G | Tier1 | 1 / 218 | |
| chr10:89693001 | A | G | 5 / 9 | p.D162G | c.485A>G | COSV64301645 | Tier1 | 1 / 218 |
| chr10:89711875 | G | A | 6 / 9 | p.G165R | c.493G>A | COSV64289126 | Tier2 | 1 / 218 |
| chr10:89711882 | C | CT | 6 / 9 | p.I168fs | c.501dupT | Tier2 | 1 / 218 | |
| chr10:89711891 | G | A | 6 / 9 | p.S170N | c.509G>A | COSV64288690 | Tier2 | 1 / 218 |
| chr10:89711899 | C | T | 6 / 9 | p.R173C | c.517C>T | COSV64288569 | Tier2 | 5 / 218 |
| chr10:89711900 | G | A | 6 / 9 | p.R173H | c.518G>A | COSV64288961 | Tier1 | 10 / 218 |
| chr10:89711917 | AG | A | 6 / 9 | p.S179fs | c.536delG | Tier2 | 1 / 218 | |
| chr10:89711971 | A | T | 6 / 9 | p.K197* | c.589A>T | Tier2 | 1 / 218 | |
| chr10:89712007 | G | T | 6 / 9 | p.G209* | c.625G>T | COSV64294737 | Tier2 | 1 / 218 |
| chr10:89712015 | C | A | 6 / 9 | p.C211* | c.633C>A | COSV64294019 | Tier1 | 1 / 218 |
| chr10:89717615 | C | T | 7 / 9 | p.Q214* | c.640C>T | COSV64290622 | Tier2 | 1 / 218 |
| chr10:89717629 | C | A | 7 / 9 | p.C218* | c.654C>A | COSV64288514 | Tier2 | 1 / 218 |
| chr10:89717630 | C | T | 7 / 9 | p.Q219* | c.655C>T | COSV64289965 | Tier2 | 1 / 218 |
| chr10:89717636 | A | T | 7 / 9 | p.K221* | c.661A>T | COSV64292017 | Tier2 | 1 / 218 |
| chr10:89717646 | T | TA | 7 / 9 | p.Y225fs | c.672dupA | COSV64293913 | Tier2 | 1 / 218 |
| chr10:89717672 | C | T | 7 / 9 | p.R233* | c.697C>T | COSV64288653 | Tier1 | 12 / 218 |
| chr10:89717678 | G | T | 7 / 9 | p.E235* | c.703G>T | COSV64291436 | Tier2 | 1 / 218 |
| chr10:89717697 | T | C | 7 / 9 | p.F241S | c.722T>C | COSV64294827 | Tier1 | 1 / 218 |
| chr10:89717698 | TG | T | 7 / 9 | p.E242fs | c.724delG | Tier2 | 1 / 218 | |
| chr10:89717700 | AGTTCCCTCAGC | A | 7 / 9 | p.E242fs | c.726_736delGTTCCCTCAGC | Tier2 | 1 / 218 | |
| chr10:89717718 | CTG | C | 7 / 9 | p.C250fs | c.750_751delTG | COSV64288359 | Tier2 | 1 / 218 |
| chr10:89717727 | GT | G | 7 / 9 | p.D252fs | c.753delT | COSV64289875 | Tier2 | 1 / 218 |
| chr10:89717756 | C | T | 7 / 9 | p.Q261* | c.781C>T | COSV64294889 | Tier2 | 1 / 218 |
| chr10:89717756 | CAG | C | 7 / 9 | p.N262fs | c.783_784delGA | COSV64289013 | Tier2 | 1 / 218 |
| chr10:89720671 | G | A | 8 / 9 | p.W274* | c.822G>A | COSV64292178 | Tier2 | 1 / 218 |
| chr10:89720678 | A | G | 8 / 9 | p.T277A | c.829A>G | COSV64298496 | Tier2 | 1 / 218 |
| chr10:89720693 | G | T | 8 / 9 | p.G282* | c.844G>T | COSV64292277 | Tier2 | 2 / 218 |
| chr10:89720709 | CAG | C | 8 / 9 | p.E288fs | c.862_863delGA | COSV64304394 | Tier2 | 1 / 218 |
| chr10:89720709 | C | A | 8 / 9 | p.S287* | c.860C>A | Tier2 | 1 / 218 | |
| chr10:89720725 | TG | T | 8 / 9 | p.G293fs | c.878delG | COSV64295414 | Tier2 | 1 / 218 |
| chr10:89720744 | G | T | 8 / 9 | p.E299* | c.895G>T | COSV64293312 | Tier2 | 7 / 218 |
| chr10:89720789 | G | T | 8 / 9 | p.E314* | c.940G>T | COSV64297686 | Tier2 | 1 / 218 |
| chr10:89720793 | ATCTAGT | A | 8 / 9 | p.Y315_V317delins* | c.945_950delTCTAGT | Tier2 | 1 / 218 | |
| chr10:89720794 | T | G | 8 / 9 | p.Y315* | c.945T>G | COSV64301587 | Tier2 | 1 / 218 |
| chr10:89720794 | TCTAGTACTTACTTTAACAAAAA | T | 8 / 9 | p.L316fs | c.946_967delCTAGTACTTACTTTAACAAAAA | Tier2 | 1 / 218 | |
| chr10:89720852 | C | T | 8 / 9 | p.R335* | c.1003C>T | COSV64288687 | Tier1 | 2 / 218 |
| chr10:89720857 | C | A | 8 / 9 | p.Y336* | c.1008C>A | COSV64294380 | Tier2 | 1 / 218 |
| chr10:89720870 | T | G | 8 / 9 | p.F341V | c.1021T>G | COSV64288696 | Tier1 | 5 / 218 |